在细胞内,核糖体依据承载遗传信息的DNA,将20种氨基酸按特定排列顺序连接数十至数千个,从而合成蛋白质。近年研究发现,存在一些核糖体难以合成的氨基酸序列。这类氨基酸序列被称为“难翻译序列”。这些会导致蛋白质合成中断的难翻译序列,对生物而言本是不利的,因此阐明其存在对生物进化产生了何种影响,具有极为重要的意义。
日本大学共同利用机关法人信息与系统研究机构国立遗传学研究所的藤原圭吾特命助教与京都产业大学的千叶志信教授等人的研究团队,发现了细菌共有的难翻译序列模式,同时证实存在一类能主动利用难翻译序列发挥作用的特殊蛋白质群。
研究团队首先通过系统性突变分析,确定出当氨基酸序列中含有精氨酸-甘氨酸-脯氨酸-脯氨酸(RGPP)或精氨酸-丙氨酸-脯氨酸-脯氨酸(RAPP)时,容易形成难翻译序列。然后通过对网罗整个细菌界的遗传信息进行全面分析,发现RGPP序列在细菌界中出现的频率最低。此外,研究团队重点关注了羧基末端附近大量存在RAPP或RGPP序列的放线菌,通过生物信息学分析证实,这些蛋白质具有被认为可用于监测细胞内外环境并帮助生物体适应环境的未知的生理功能。
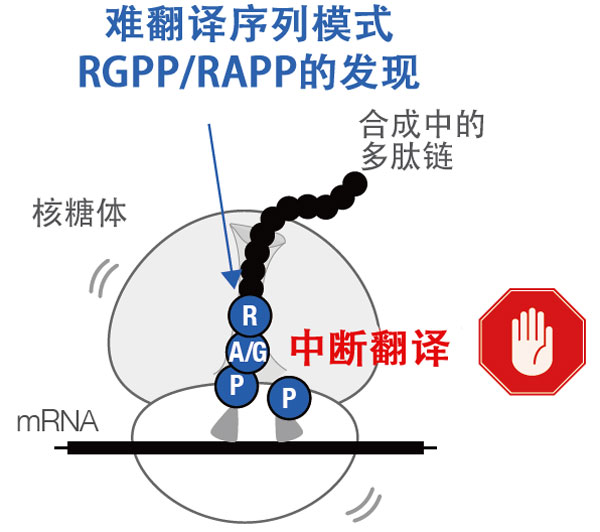
核糖体通过翻译信使RNA(mRNA)来合成蛋白质。研究发现,在许多细菌中,存在会导致核糖体蛋白质合成中断的难翻译序列的共同模式,并探究了其功能。
此次研究成果为理解遗传信息的进化、基因表达及翻译的分子机制提供了基础理论依据。同时有望为利用细菌及微生物生产有用化合物的“生物制造”以及抗生素研发提供重要助力。(TEXT:中条将典)
原文:JSTnews 2026年3月号
翻译:JST客观日本编辑部
【论文信息】
期刊:The EMBO Journal
论文:Evolutionary Adaptation of Bacterial proteomes to Translation-Impeding Sequences
DOI:10.1038/s44318-025-00651-6